Modificar la vida: avances de la biología sintética
Guillermo Cárdenas Guzmán

Foto: Steve Jurvetson
Como si manipularan piezas del juego Lego, los científicos diseñan y ensamblan circuitos biológicos que no existen en la naturaleza. Con ellos buscan producir a bajo costo vacunas, fármacos, biocombustibles y nuevos materiales.
Un biotecnólogo se sienta frente a la pantalla de su computadora. Da un clic y ante él se despliegan decenas de páginas con bases de datos sobre microorganismos. Entre ellos selecciona una bacteria. Ahora accede a otra página repleta de información genética. Asistido por un programa de cómputo y como si editase un texto se dedica a copiar y pegar grupos de letras que representan fragmentos de ADN para dar forma a un novedoso diseño. Estos fragmentos en particular son circuitos genéticos, esto es, conjuntos de genes que dan lugar al “encendido” o “apagado” de otros genes.
Como un niño que manipula las piezas de un rompecabezas tipo Lego, el científico continúa con la selección y ensamblaje de combinaciones de circuitos genéticos que le permitirán armar un microorganismo “a la carta”, que no existe en la naturaleza y que podrá desarrollar funciones preprogramadas.
Concluido el ensamblaje de genes el investigador lo usa en el laboratorio para producir el nuevo microorganismo con un propósito específico que puede ser generar biocombustibles, detectar enfermedades genéticas o eliminar tumores malignos. Con los avances de la biología sintética esta escena ya no parece de ciencia-ficción.
Cabras y arañas
En 2012 investigadores de la Universidad Estatal de Utah, Estados Unidos, encabezados por Randy Lewis, anunciaron la culminación exitosa de un audaz experimento para producir auténticas quimeras vivientes: cabras a las que se les introdujo un gen de araña para que produjeran en su leche una proteína indispensable para fabricar tela de araña.
Para producir telaraña a escala masiva se necesitaría criar y “ordeñar” millones de estos artrópodos. Pero el profesor de biología molecular Randy Lewis decidió probar una ruta más sencilla: cuando sus cabrarañas comenzaran a lactar, simplemente recolectaría y purificaría su leche para obtener la proteína deseada.
No podían faltar las críticas a éste y otros experimentos similares con animales transgénicos: muchos acusaron a Lewis de “jugar a ser dios” o de alterar el orden natural. Lo cierto es que, con todo y su espectacularidad, los avances de la ingeniería genética podrían palidecer pronto ante la gama de posibilidades que está abriendo la biología sintética.
Ahora la intención no es únicamente modificar o reconfigurar a los organismos existentes, sino diseñar —con el apoyo de programas de cómputo y la gran cantidad de información que deriva del auge explosivo de las ciencias genómicas— otros con características deseables, que pueden encontrarse o no en la naturaleza.
“En este campo no sólo se hacen pequeñas modificaciones en la información genética, sino que también se diseñan, manipulan, simulan e introducen circuitos genéticos a los organismos”, señalan Daniel Aguilar e Isabel Ángeles en su artículo “Biología sintética: diseñando sistemas biológicos con piezas genéticas”, publicado en la revista BioTecnología en 2012.
Con este enfoque —plantean los autores del artículo— “se están abordando distintos problemas tecnológicos como nuevas formas de síntesis y producción de biocombustibles, biofármacos y nanoestructuras”.
 Randy Lewis dirigió un experimento audaz: introducir un gen de araña a cabras para que produjeran en su leche una proteína indispensable para fabricar tela de araña. Foto: Utah State University.
Randy Lewis dirigió un experimento audaz: introducir un gen de araña a cabras para que produjeran en su leche una proteína indispensable para fabricar tela de araña. Foto: Utah State University.
 Craig Venter (izq.) mostró que era posible diseñar un genoma mediante computadora, fabricarlo e implantarlo en una célula que a su vez produjo otra capaz de replicarse siguiendo las “instrucciones” del genoma sintético. Foto: J. Craig Venter Institute.
Craig Venter (izq.) mostró que era posible diseñar un genoma mediante computadora, fabricarlo e implantarlo en una célula que a su vez produjo otra capaz de replicarse siguiendo las “instrucciones” del genoma sintético. Foto: J. Craig Venter Institute.
 Con el trabajo de Jay Keasling (izq.) se demostró que es viable transferir entre organismos la capacidad de fabricar ciertas proteínas y enzimas, lo cual abre la posibilidad de transformar carbohidratos en combustibles de bajo costo. Foto: JBEI/Jay Keasling.
Con el trabajo de Jay Keasling (izq.) se demostró que es viable transferir entre organismos la capacidad de fabricar ciertas proteínas y enzimas, lo cual abre la posibilidad de transformar carbohidratos en combustibles de bajo costo. Foto: JBEI/Jay Keasling.
Organismos artificiales
Cuando en 2010 el famoso científico californiano Craig Venter dio a conocer el ensamblaje y autorreplicación de una bacteria Mycoplasma mycoides —cuyo genoma artificial fue inoculado en la carcasa de otra bacteria desprovista de su propio ADN— el mundo científico se conmocionó (véase ¿Cómo ves? No. 140). El exitoso experimento de Venter mostró que era posible diseñar un genoma mediante computadora, fabricarlo con los elementos químicos necesarios en el laboratorio e implantarlo en una célula que a su vez produzca otra nueva capaz de replicarse siguiendo las “instrucciones” del genoma sintético. Sin embargo, para entonces la biología sintética ya había dado otros pasos importantes.
“El reto que enfrentó Craig Venter fue de tipo técnico, mas no conceptual, ya que pudo construir cromosomas enteros para la bacteria Mycoplasma mycoides”, explica en entrevista Daniel Aguilar. De acuerdo con este biotecnólogo egresado del Instituto de Investigaciones Biomédicas de la UNAM, el mérito de Venter es que antes de ese trabajo no se habían producido o sintetizado fragmentos completos muy largos de ADN en el laboratorio.
En 2003 Jay Keasling, de la Universidad de California, Estados Unidos, logró introducir un circuito genético para producir en la bacteria Escherichia coli un precursor químico de la artemisinina, fármaco usado contra la malaria. Y en 2010 la compañía estadounidense LS9 modificó genéticamente a este mismo microorganismo para que produjera alcanos y alquenos, que son los constituyentes básicos de la gasolina, el diesel y la turbosina. Este trabajo demostró que es viable transferir entre organismos la capacidad de fabricarciertas proteínas y enzimas, lo cual abre la posibilidad de transformar carbohidratos en combustibles de bajo costo.
En México también hay grupos que han incursionado en esta disciplina. Es el caso del Laboratorio de Biología Sintética y Biosistemas del Centro de Investigación y Estudios Avanzados (Cinvestav) Unidad Irapuato. En este laboratorio, según explica en entrevista su titular, Agustino Martínez Antonio, se siguen líneas de investigación enfocadas a conocer cómo funcionan los circuitos genéticos y a hacer ingeniería con esas piezas.
“Queremos obtener los elementos mínimos para hacer un sistema autorreplicable; es decir, una molécula de ADN con los genes necesarios para que se forme una proteína o un complejo de proteínas y pueda hacer copias, como un robot que se autoensambla, pero a nivel molecular”.
El grupo de trabajo del doctor Martínez, que ya tiene convenios con empresas mexicanas, asimismo busca ensamblar circuitos genéticos que sirvan para producir a menor costo compuesto usados en la industria alimentaria como licopeno, betacaroteno y melanina, además de biocombustibles.
Organismos a la carta
La biología sintética se define como el diseño y la construcción de sistemas biológicos y bioquímicos que realicen funciones nuevas o mejoradas, las cuales puedan aprovecharse en la producción de fármacos, vacunas y biocombustibles, entre muchas otras aplicaciones. Está sustentada en una amplia gama de disciplinas —incluida la informática— y metodologías para diseñar moléculas, construir circuitos genéticos y ensamblar organismos simples.
La Red Mundial de Academias de Ciencias (que incluye a la Mexicana de Ciencias, AMC) emitió en 2014 una declaración titulada “Concretando el potencial global en biología sintética: oportunidades científicas y buen gobierno”. En ese documento (que puede consultarse en www.interacademies. net) la Red recomienda, entre otras medidas, apoyar la investigación básica en biología sintética, además de que se revisen continuamente los aspectos éticos y las cuestiones sociales que emergen de la disciplina.
 Agustino Martínez Antonio en el Laboratorio de Biología Sintética y Biosistemas del Cinvestav, Unidad Irapuato. Foto: Agustino Martínez.
Agustino Martínez Antonio en el Laboratorio de Biología Sintética y Biosistemas del Cinvestav, Unidad Irapuato. Foto: Agustino Martínez.
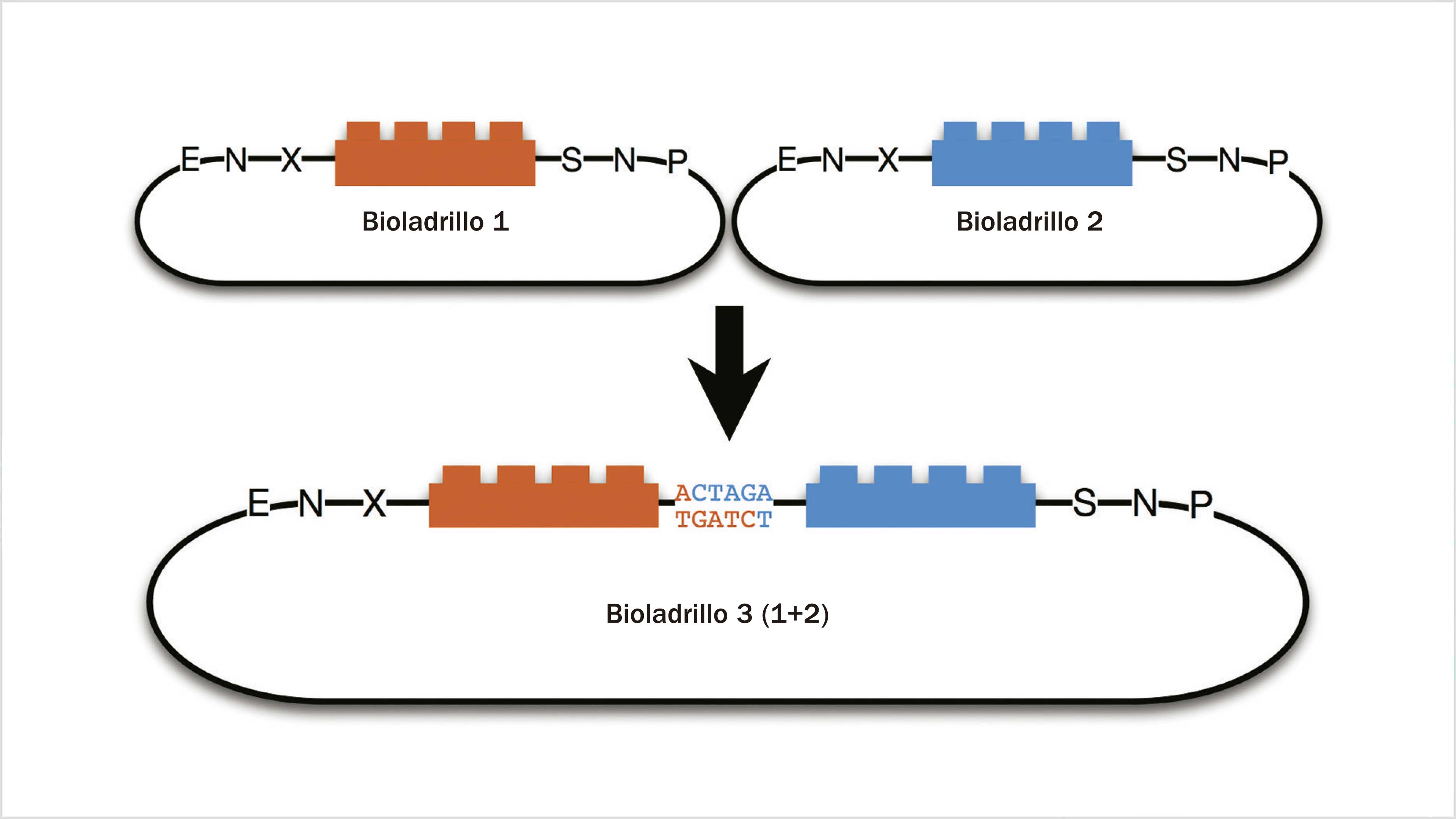 Ensamblaje de bioladrillos.
Ensamblaje de bioladrillos.
Otro ladrillo en la pared
Algunos grupos dentro de la biología sintética han puesto sus esperanzas un paso más allá: hacer accesible a cualquier persona tanto el “inventario” de piezas del rompecabezas de la vida como los procedimientos para ensamblarlas. La meta es que los avances de esta ciencia sirvan al interés de toda la sociedad.
Una de las iniciativas más audaces en esa línea es de la Fundación Biobricks (BBF), asociación no lucrativa fundada en 2006 en el Instituto Tecnológico de Massachusetts (MIT), Estados Unidos, a iniciativa del biólogo e ingeniero en computación Tom Knight. Biobricks busca establecer una plataforma común con estándares técnicos para la fabricación de piezas biológicas sintéticas intercambiables, tal como se hace al construir autos o circuitos electrónicos.
“Vislumbramos un mundo en el que científicos e ingenieros trabajen juntos utilizando partes biológicas estandarizadas disponibles gratuitamente que sean seguras, éticas, efectivas y públicamente accesibles para aportar soluciones a los problemas que enfrenta la humanidad”, señala un comunicado de BBF en su página web.
El protocolo de ensamblaje 10, desarrollado por Knight y basado en el uso de enzimas de restricción, que funcionan como “tijeras moleculares” para cortar fragmentos de ADN, fue el primero en usarse. Este método permite construir —siguiendo con la analogía del juego Lego— módulos que son funcionales, pero tiene ciertas limitaciones. Por ejemplo, al ligar dos bioladrillos se producen entre ellos pares de bases “cicatriz” que no son reconocidas por las enzimas de restricción (no “encajan” completamente en el rompecabezas) lo cual impide la formación de proteínas quiméricas, es decir, resultantes de la fusión de dos o más genes que originalmente codificaban para dos proteínas distintas.
Por ello, en la última década se introdujeron otros estándares más eficaces que permiten superar los obstáculos que limitan el armado de piezas biológicas, como el Silver y el Friburgo.
El primero —introducido por la investigadora Pamela Silver, de la Universidad de Harvard y conocido también como Biofusión— permite reducir la longitud de la “cicatriz” de ocho a sólo seis “letras” del ADN, y con ello la fusión de proteínas.
El otro método, desarrollado por un grupo en la Universidad de Friburgo, Alemania, introdujo el uso de enzimas de restricción adicionales para cortar los fragmentos genéticos. Aunque conserva el tamaño de las “cicatrices” en seis pares de bases, éstas codifican otras proteínas que resultan más estables.
Otros métodos de amplificación y síntesis de ADN como el ensamblaje Gibson o el SLIC (Sequence and Ligation Independent Cloning) permiten armar múltiples partes biológicas sin necesidad de cortar o pegar segmentos, ya que no requieren enzimas de restricción, según comenta Daniel Aguilar. Tanto el método Gibson —inventado en 2009 por Daniel Gibson, del J. Craig Venter Institute— como el SLIC —desarrollado en 2007 por los investigadores Mamie Li y Stephen Elledge— hacen factible unir muchos fragmentos de ADN en una sola reacción, sin necesidad de que las piezas sean compatibles. Este último posibilita un ensamblaje más eficiente y reproducible de ADN recombinante con cinco o incluso 10 fragmentos de manera simultánea, según describen sus autores en un artículo, publicado en la revista Nature Methods en febrero de 2007.
“Con estas dos técnicas sólo se necesitan nucléotidos (las “letras” del código genético, A, C, G, T) que tengan secuencias en común con los dos pedazos que se van a pegar y luego, mediante una reacción en cadena de la polimerasa (RPC) se amplifica todo el segmento”, detalla Aguilar. La RPC permite obtener copias múltiples de fragmentos de ADN; la desarrolló el bioquímico estadounidense Kary Mullis y por ello obtuvo el premio Nobel de Química en 1993.
Red de colaboración
La Fundación Biobricks desarrolla y promueve estándares técnicos para la fabricación de piezas biológicas sintéticas. Estas piezas estarán disponibles en una base de datos. Los principales logros de esa fundación incluyen:
- Un acuerdo público, establecido en 2011, que permite legalmente a individuos, compañías e instituciones el intercambio y empleo de piezas biológicas (https://biobricks.org/ bpa/).
- Una red de colaboración entre profesionales del área, el Espacio Abierto Internacional para el Avance de la Biotecnología, fundado en 2009 (http://biofab.synberc.org/).
- Un si t io wiki abier to (http://openwetware.org/wiki/) que facilita la enseñanza, aprendizaje y difusión de conocimientos de biología, ingeniería genética y áreas afines.
- Una serie de conferencias sobre biología sintética, también disponibles en: http://biobrick.org/ programs/sbx-0-conference-series/.
 George Church, pionero de la biología sintética y la genómica personalizada. Foto: Steve Jurvetson.
George Church, pionero de la biología sintética y la genómica personalizada. Foto: Steve Jurvetson.
Reinventar la naturaleza
Tres siglos antes de nuestra era Aristóteles sostuvo que el arte imita a la vida. La ciencia del siglo XXI, a través de la biología sintética, también puede asumir esta máxima, ya que busca emular ciertas características y funciones de organismos que han sido moldeadas a lo largo de millones de años de evolución.
Pero hoy los científicos no se conforman con describir pasivamente las secuencias genéticas naturales de los organismos. Algunos de ellos, como el genetista George Church, profesor de la Escuela de Medicina en la Universidad de Harvard, ya trabajan en la “edición” y “corrección” de la vida. Church, pionero de la biología sintética y la genómica personalizada, considera que mediante la alteración dirigida del código genético y la “creación” de nucleótidos sintéticos pronto será viable modificar la vida desde sus bases mismas, generar nuevas formas de ella e incluso diseñar organismos simples y después otros complejos —incluidos los humanos— que sean resistentes a infecciones bacterianas o virales.
Suena a ciencia-ficción, pero Church está convencido de que al paso en que se reducen los costos de la clonación y secuenciación de genes y avanzan estas tecnologías, pronto sería incluso factible “revivir” especies desaparecidas, como los neandertales, como señaló en entrevista a la revista alemana Der Spiegel (18 de enero de 2013).
El genetista estadunidense —quien en los años 80 aportó el primer método directo de secuenciación genómica, que más tarde impulsaría el Proyecto del Genoma Humano— ha planteado asimismo la posibilidad de construir plantas con nucleótidos sintéticos. Estos vegetales serían más que especies exóticas: su información genética sería, por decirlo así, “incompatible” con el código de la vida que la naturaleza ha forjado en millones de años de evolución. Sus genes no podrían transferirse a otros vegetales debido a que ningún organismo natural tendría el “manual de instrucciones” para leerlos y activarlos.
Church dio a conocer en un artículo publicado en la revista Science el 15 de julio de 2011 un método para cambiar radicalmente el genoma de una bacteria, en vez de sólo realizar copias, como ha hecho el equipo de Craig Venter.
Con este procedimiento, conocido coloquialmente como intervención masiva paralela, los investigadores lograron no solamente “leer” los códigos genéticos, sino editar cientos de letras en una forma rápida y mucho menos costosa en comparación con el método de Venter, consistente en crear un genoma artificial completo, cuyo costo se estima en millones de dólares.
El equipo de Church, para seguir con la analogía de la edición, sustituyó una de las “palabras” del código genético de la bacteria Escherichia coli con otra equivalente, es decir, con una especie de sinónimo. La estructura remplazada, que está formada por una secuencia de tres nucleótidos, se denomina técnicamente codón.
Los científicos sustituyeron un codón denominado stop, que funciona como signo de puntuación pues provee las instrucciones a la maquinaria celular de la bacteria para que deje de ligar aminoácidos. Con dos métodos distintos cambiaron la secuencia TAG, que aparece 314 veces en el genoma de E. coli, por otra que contiene las “letras” TAA. Este pequeño cambio resultó inocuo, pero no insignificante: al cambiar así el código genético de la bacteria las funciones de ésta quedan intactas, pero los virus invasores —que dependen por completo de su huésped para replicarse, ya que no pueden elaborar sus propias proteínas— no podrán leer dicho código alterado ni apropiarse de la maquinaria celular.
Concurso para diseñar un sistema biológico
La Competencia Internacional de Máquinas Genéticamente Modificadas (iGem por sus siglas en inglés) es un concurso anual de biología sintética que surgió en 2003 en el Instituto Tecnológico de Massachusetts, Estados Unidos, y ahora está a cargo de una fundación. Originalmente el concurso era sólo para estudiantes de licenciatura, pero en 2011 se amplió a estudiantes de bachillerato y emprendedores. Al inscribirse, los concursantes reciben un kit de partes biológicas o bioladrillos con las que deben diseñar un sistema biológico durante el verano. México ha participado en varias ediciones de la competencia. En 2010 estuvieron entre los ganadores un grupo formado por estudiantes de la UNAM y del Instituto Politécnico Nacional y un grupo del Instituto Tecnológico de Estudios Superiores de Monterrey. Entre los proyectos destacados de la competencia hay un biodetector de arsénico y un sustituto de glóbulos rojos.
 Miembros del equipo iGEM-TecMonterrey. Foto: iGEM.
Miembros del equipo iGEM-TecMonterrey. Foto: iGEM.
Regulación indispensable
Al tomar el control sobre la evolución y diseñar la secuencia apropiada de letras del código genético, los científicos pretenden construir organismos a la medida, para satisfacer una gran variedad de necesidades en campos como la farmacología (vacunas, hormonas, biomarcadores), la agricultura (biocombustibles, plantas resistentes a plagas) y la ciencia de materiales (nanoestructuras con características mejoradas), entre otras.
“Estamos en un punto de la ciencia y la tecnología donde los humanos podemos duplicar y mejorar lo que la evolución ha hecho”, escribe Church en su libro Regénesis, cómo la biología sintética reinventará la naturaleza y a nosotros mismos. “Podemos convertir lo inorgánico en orgánico, leer e interpretar genomas y también modificarlos”. Pero no todo el panorama luce promisorio: tales manipulaciones han despertado temores por sus posibles riesgos y consecuencias en la salud y el medio ambiente si no son supervisadas y reguladas adecuadamente. ¿Qué sucedería, por ejemplo, si alguno de esos organismos sale del control del laboratorio o cae en manos de terroristas? ¿Cómo serían sus interacciones con el ambiente? Otro tema que preocupa es el de sus posibles efectos secundarios u otros riesgos que aún no podemos vislumbrar con claridad, dado el incipiente desarrollo de la biología sintética. Una de las grandes figuras de esta disciplina, Drew Endy, del Instituto Tecnológico de Massachusetts, ha reconocido que la misma no alcanzará todo su potencial hasta que los científicos puedan predecir con precisión cómo funcionarán los circuitos genéticos dentro de una célula.
“Desafortunadamente, nuestra habilidad para diseñar sistemas biológicos en forma rápida y confiable y que se comporten como lo esperamos sigue siendo limitada”, escribió Endy en su artículo “Fundamentos de la ingeniería biológica”, publicado en 2005 en la revista Nature.
Tales inquietudes, así como la falta de regulación internacional en la materia, han estimulado el debate y conducido a diversas organizaciones sociales y grupos ambientalistas como Amigos de la Tierra, ETC y Econexus a plantear la necesidad de establecer lineamientos y códigos para normar la labor de los biólogos sintéticos. “La biología sintética incluye muchas técnicas nuevas, experimentales, de las que se comprende muy poco, y esto incrementa en gran medida los riesgos a la salud humana, la alimentación y las formas de sustento”, señaló al respecto Helena Paul, directora de Econexus. Pero hay avances. El año pasado, durante la Doceava Conferencia de las Partes de la Organización de Naciones Unidas (COP12), celebrada en Corea, 194 países suscribieron el Convenio sobre Diversidad Biológica que contempla, entre otras cosas, establecer una regulación internacional en la materia basada en la protección al ambiente, la cooperación y la valoración científica de posibles riesgos.
Más información
- Asociación Mexicana de Biología Sintética: www.biosintetica.mx
- Schmidt W., Charles, “Las implicaciones de un nuevo campo para la salud ambiental”, Salud
Pública de México, 2010.
Guillermo Cárdenas Guzmán es periodista en temas de ciencia y salud. Ha colaborado en diversos suplementos y medios culturales y fue reportero y editor de secciones de la revista Muy interesante














